Notre laboratoire étudie les processus évolutifs impliqués dans la plasticité des génomes de plantes ainsi que les mécanismes moléculaires permettant de réguler l’expression des gènes, principalement en situation de stress. Nous utilisons des approches de génomique, bioinformatique, biologie théorique et modélisation, génétique, biochimie, biologie cellulaire et moléculaire.
Le laboratoire est structuré en sept équipes de recherche :
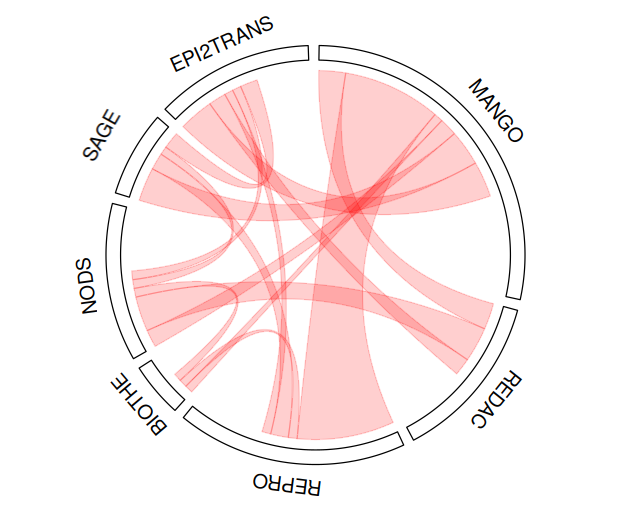
Illustration des collaborations entre les équipes par la représentation du nombre d'articles publiés en commun sur les années 2020 - 2024 :
La liste des projets financés portés par le LGDP est accessible : liste des projets financés.
Le laboratoire est structuré en sept équipes de recherche :
| 2020 - 2024 | 2025 - 2029 | Dénomination de l'équipe |
| SipTRiP | REPRO | Reprogrammations post-transcriptionnelles en réponse au stress chez les plantes |
| GRRIP | SAGE | Silencing et régulation génique dans les organismes photosynthétiques |
| MANGO | MANGO | Mécanismes d’adaptation et génomique |
| REDAC | REDAC | Redox, Développement et Adaptation aux Contraintes |
| NoDS | NODS | Nucléole : développement et réponse aux stress |
| MEAC | EPI2TRANS | Régulations épigénétiques de la transcription et des transposons |
| BT | BIOTHE | Biologie théorique |

La liste des projets financés portés par le LGDP est accessible : liste des projets financés.
Mise à jour le 21 mars 2025









