Thématiques de recherche
L'information génétique codée par l'ADN est transcrite sous forme d'ARN messagers (ARNm). Ces copies de l’information génétique sont ensuite traduites par les ribosomes en protéines qui constituent les effecteurs de nombreuses et diverses fonctions cellulaires. Chaque strate de ce flux d’information doit être finement contrôlée et modulée pour permettre à un organisme de se développer et s’adapter à son environnement. Notre groupe s’intéresse à l’étude des mécanismes de régulation génique au sens large qui impliquent soit des modifications épigénétiques de l’ADN et de la chromatine, des modifications épitranscriptomiques des bases de l'ARNm, l'intervention de protéines de liaison à l'ARNm ou encore la régulation génique guidée par des petits ARN via les protéines Argonautes.Régulation épitranscriptomique chez les plantes.
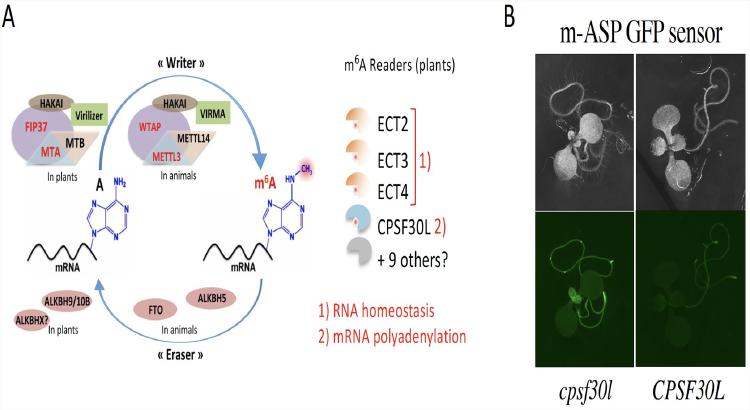
Fig 1: Mécanismes de régulation épitranscriptomique chez les plantes (A), senseur fluorescent de l’activité de la voie de maturation des ARNm dépendante du m6A in planta (B).
L’activité de l’ARNm chez les eucaryotes peut être contrôlée par la modification chimique de la base adénosine en N6-methyladénosine (ou m6A), un mécanisme connu sous le nom d'épitranscriptomique. La marque m6A est déposée sur l’ARNm de manière co-transcriptionnelle par un complexe de marquage (writer), et impacte le destin des ARNm de diverses manières en recrutant des protéines lectrices du m6A (readers/ECT) qui présentent un domaine de type YTH (Fig 1A). En particulier, notre équipe a identifié chez Arabidopsis un mécanisme de contrôle de la maturation de l’ARNm assisté par la marque m6A (m-ASP) qui assure la fidélité du transcriptome grâce à l’action d’une protéine YTH spécifique, nommée CPSF30L (Fig 1A).
Nous nous intéressons actuellement à l'identification de nouveaux acteurs de cette voie de régulation épitranscriptomique chez Arabidopsis. Dans ce but, nous avons construit un système rapporteur fluorescent du fonctionnement de cette voie de régulation (Fig 1B) qui est actuellement utilisé dans un criblage génétique. Les candidats identifiés seront analysés par un large panel d'approches biochimiques et moléculaires (IP-MS, CLNIP-MS, ChIP-seq, Nanopore DRS....).
Rôles de protéines de liaison à l'ARN dans la régulation génique.

Fig 2. Phénotype du mutant msil chez Arabidopsis A) et analyse intégrative des protéines Musashi-like/MSIL chez les plantes B).
L'expression génique peut être modulée au niveau post-transcriptionnel par l'intervention de protéines de liaison à l'ARNm (RBP pour RNA-Binding Protein). Il existe un très grand nombre de RBP chez les plantes qui sont impliquées à toutes les étapes de la formation, de la maturation et de l’expression de l’ARNm. Notre équipe s’intéresse à une famille de RBP homologues au régulateur traductionnel animal Musashi, nommées Musashi-like/MSIL, qui contrôlent divers aspects du développement d'Arabidopsis, et notamment la formation de la paroi cellulaire secondaire dans la tige de l'inflorescence (Fig 2A). Nous utilisons actuellement une combinaison d'approches moléculaires, biochimiques, génétiques et chimiques pour mieux comprendre la fonction et le mécanisme d’action des protéines MSIL chez Arabidopsis, mais également chez les arbres ou les céréales qui présentent des parois secondaires avec des structures chimiques différentes (Fig2 B).
Etude du rôle des protéines effectrices Argonautes dans le RNA silencing et de leur régulation.
Des voies de régulation génique utilisant des petits ARN interférants, connues sous le nom de RNA silencing, sont largement conservées dans les organismes vivants, et leur identification a été récompensée par deux prix Nobel en 2006 et 2024. Un acteur essentiel du RNA silencing est la protéine Argonaute/AGO qui, en association avec l’ARN interférant, régule l’expression génique à un niveau transcriptionnel ou post-transcriptionnel (Fig 3A). Les plantes se distinguent par un grand nombre de protéines AGO, qui peuvent être classées en deux groupes principaux: la famille AGO1, dont les membres lient des petits ARNs de 21 nt (miRNA) et régulent le développement des plantes et leur réponse à l'environnement via des mécanismes de régulation post-transcriptionnelle (Fig 3B), et la famille AGO4, dont les membres lient des petits ARNs de 24 nt et répriment l’expression génique à un niveau transcriptionnel. Le décryptage du mode d'action de cette superfamille d'effecteurs est donc crucial pour la compréhension des mécanismes de RNA silencing.

Fig 3. Le RNA silencing est un levier de contrôle très spécifique largement conservé chez les organismes vivants. Ce mécanisme permet de réduire l'expression de gènes grâce à l'action de protéines Argonaute guidées par des petites molécules d’ARN sur leurs cibles complémentaires (représenté ici, un ARNm ciblé par la voie PTGS, Post-Transcriptional Gene Silencing) A), et phénotype développemental drastique du mutant nul ago1 chez Arabidopsis B).
L'étude de l'activité des protéines AGO chez les plantes se décompose en deux volets actuellement dans l'équipe, dont une recherche non biaisée des partenaires de ces protéines et une analyse fine de la régulation de la protéine AGO1.
1) Le recrutement et/ou l’activité des protéines AGO dans le RNA silencing nécessitent des protéines partenaires spécifiques qui présentent des motifs conservés de type WG (tryptophane-glycine). Nous avons précédemment développé une approche bioinformatique pour identifier de nouvelles protéines à motif WG susceptibles de recruter/travailler avec les protéines AGO chez les plantes. Nous poursuivons actuellement l'analyse fonctionnelle de ces candidats dans l’objectif de caractériser de nouvelles activités de RNA silencing chez les plantes.
2) L'activité de la protéine AGO1 est finement contrôlée à plusieurs niveaux. Parmi les mécanismes impliqués, les modifications post-traductionnelles (PTM) constituent un mode de régulation particulièrement intéressant, compte tenu des processus biologiques fondamentaux régulés par AGO1 (Fig 3B). Il s'agit de modifications chimiques réversibles ou irréversibles qui sont déposées sur la chaîne latérale des acides aminés comme, par exemple, des groupes méthyles ajoutés aux chaînes latérales de certaines arginines par l'action des arginine/R méthyltransférases/PRMT (R-met). Les PTM peuvent moduler à la fois le devenir des protéines (renouvellement, localisation) et/ou leur fonction (repliement, activité, réseau de partenaires), et ce de façon dynamique et énergétiquement peu coûteuse. Nos travaux sur la plante modèle Arabidopsis thaliana ont montré qu'AGO1 est méthylé par différents membres de la famille des protéines PRMT, révélant une double signature R-met unique. Nous développons actuellement un projet visant à comprendre la pertinence biologique et fonctionnelle de ces modifications R-met pour l'action d'AGO1 et, plus largement, pour les voies de RNA silencing chez les plantes. Nous utilisons une grande variété d'approches, comme le phénotypage de plantes en conditions normales ou de stress ou des techniques biochimiques et moléculaires, adaptées en particulier aux petits ARNs (stem-loop QPCR, smallRNA seq...).
Mots clés : épigénétique, epitranscriptomique, transcription, Argonaute, miRNA, m6A, RBP, Arginine méthylation, développement, adaptation à des facteurs biotiques et abiotiques.
Projets financés
- ANR MUSAWALL (2023-2028). Rôle et mécanismes d'action des protéines de type Musashi dans le contrôle de la synthèse des polysaccharides de la paroi secondaire chez les plantes. Coordinateur : Thierry Lagrange (LGDP, CNRS), Partenaires : Richard Sibout (BIA, CNRS/INRAe) ; Fabien Mounet (LRSV, UT3).
- ANR ALGALVIRUS (2017-2022). Adaptations Génomique des Algues Marines aux Virus. Coordinateur Nigel Grimsley (BIOM,CNRS), Partenaires: Thierry Lagrange (LGDP, CNRS); Olivier Jaillon (Genoscope, CEA).
- Bonus Qualité Recherche/BQR UPVD (2024-25) - La voie R-met, régulateur global de l’immunité chez les plantes ? Jacinthe Azevedo-Favory.
- Projet Central Labex TULIP (2022) – Analyse fonctionnelle de protéines de type Musashi chez Arabidopsis thaliana. Natacha Bies-Etheve.
- Projet Central Labex TULIP (2020) - Analyse de l'impact de l'enzyme PRMT5 sur la protéine AGO1 chez A. thaliana. Jacinthe Azevedo-favory.
Membres
Anciens membres
- Clément Barré-Villeneuve
- Alicia Kairouani
Publication par collection
- Articles
-
- Communications dans un congrès et posters
-
- Thèse et HDR
-









